小果的单日小技巧DAY5:预测某样本亚型对免疫治疗的响应step3
生信人R语言学习必备
立刻拥有一个Rstudio账号
开启升级模式吧
(56线程,256G内存,个人存储1T)

-
终于来到最后一步啦!前两期我们完成了转录组数据的标准化和相关文件的输出,本期我们进行最后一个步骤(仍旧是在服务器上运行):
Step1:Rscript preTIDE.R 亚型转录组数据进行标准化。
Step2:Rscript readTIDE.R 表型文件 TIDE输出 样本转录组 样本信息 TCGA中该类癌症全部样本转录组数据(剔除低表达)
Step3: Rscript readsubmap.R submap网站得到的矩阵中的16个pvalu
一、 真的是最后一口了
【后台使用方法】
/media/desk16/zhl/miniconda3/envs/bio/bin/Rscript/media/desk16/zhl/tools/zhl106TIDE/example_and_coad/preTIDE.R/media/desk16/zhl/tools/zhl106TIDE/example_and_coad/easy_input_expr.txt
二、开吃
如有非文件类参数,点击 输入参数对应的值,默认比如 pvalue值是0.05 gene 值是 TP53
输入文件名:无输入其他参数:输入参数1:'0.94,0.45,0.97,0.001,0.28,0.26,0.19,0.99,0.98,0.31,0.92,0.007,0.31,0.16,0.34,0.93'
【所需文件展示】
该矩阵得自submap网站输出,将其中pvalue作为输入

生成文件展示(做了一个热图):
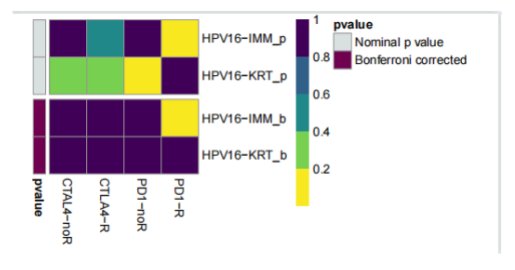
就好啦,到此结束。让我们回顾一下整个过程吧:
第一步,我们对亚型转录组数据进行标准化处理,以确保数据的一致性和可靠性,从而提高TIDE预测结果的准确性。
第二步,我们们输入了表型文件、TIDE输出文件、样本转录组数据、样本信息,以及TCGA中该类癌症全部样本的转录组数据(剔除低表达的基因)这5个文件,将TIDE算法输出的预测结果与实际样本信息进行比较,从而验证TIDE算法对免疫治疗响应的预测能力,并确定对于特定类型的癌症,TIDE算法是否适用。
第三步,读取submap算法得到的16个p值,以便进行后续的数据分析和可视化。在使用submap算法预测单个样本或者某亚型对免疫治疗的响应可能性时,submap算法会将该样本或者该亚型的基因表达谱与已有的免疫治疗数据集进行比较,得到一组16个p值,分别对应16种不同的免疫治疗反应类型。这16个p值用来表示该样本或者该亚型对这16种免疫治疗反应类型的响应可能性,p值越小则响应可能性越高。
小果吃饱学会了,你呢?
有其他分析需求可以查看生信云平台云生信 – 学生物信息学 (biocloudservice.com)
使用服务器预测某样本亚型对免疫治疗的响应可联系微信:18502195490

微信号 | 18502195490
知乎 | 生信果
点击“阅读原文”立刻拥有
↓↓↓