【一文一分钟】快速看懂GSEA结果!
点击蓝字
关注小图
小图在上一篇文章:GSEA富集分析——看了之后,小学三年级的妹妹都学会了!中,介绍了如何使用 GSEA进行富集分析。
有小伙伴纷纷反映,GSEA结果不会解读
那么好,咳咳~小图【一文一分钟】课堂开课
今天小图要解决的问题便是:GSEA 的分析结果怎么看?
话不多说~现在开始
小图收到GSEA分析结果后,打开GSEA文件夹,可以通过搜索“index”,查看GSEA分析结果:
点击index.html

网页报告中下划线部分都可以点击,链接到其他网页或者文件查看具体信息。
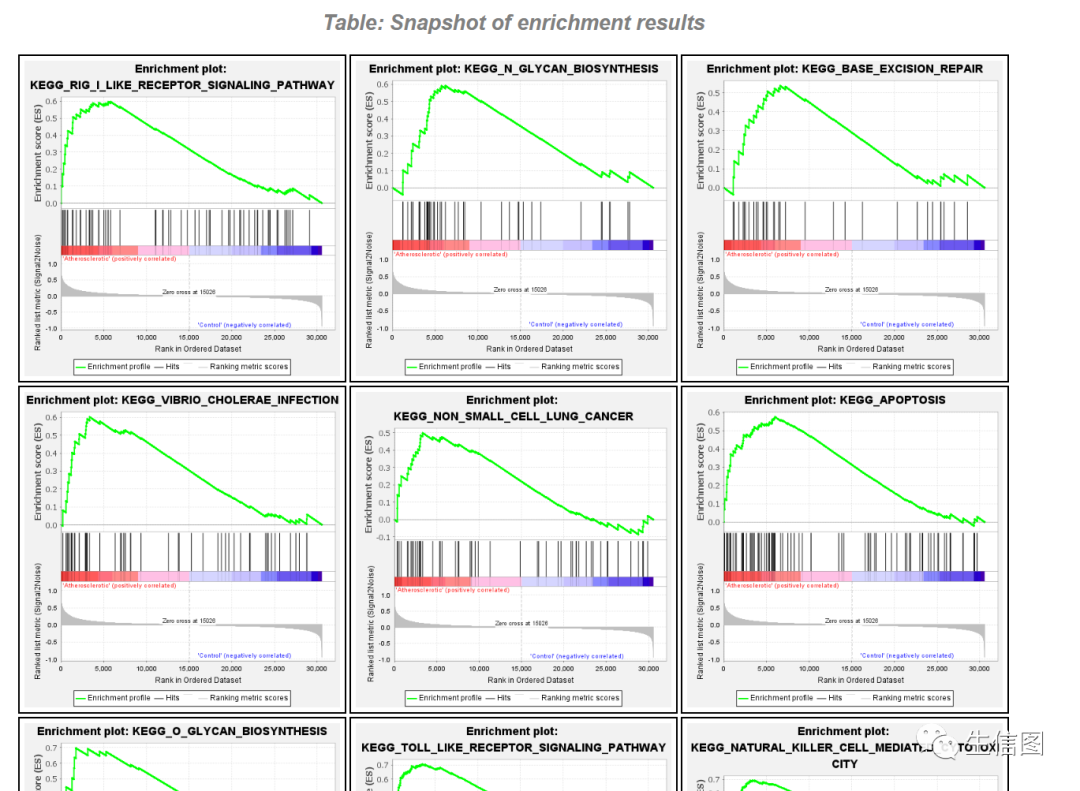
点击Snapshot会出现这114条通路的条形码富集图,如下:
点击enrichment results in html format则会显示这114条通路的富集详情:
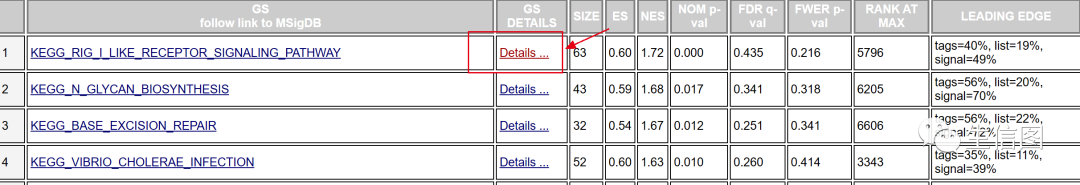
读到这里,想必图中的缩写小伙伴看的一头雾水吧,小图来一一道来
GS:基因集的名称(GO term或KEGG pathway名称)
Size:通路/条目下包含的基因数目(经过条件筛选后的值)
ES:富集得分(enrichment score)
NES:ES的标准化值(normalized enrichment score),同时考虑基因集的个数及基因数目,NES的值代表该基因集中的基因在整体基因排序列表中的富集程度。简单理解NES为正值基因集上调,负值基因集下调。
NOM p-val:P-value,针对ES的排列检验,表示基因集富集的显著性
FDR q-val:FDR法校正的p值
FWER p-val:用FWER法(Bonferonni校正)校正后的P值
RANK AT MAX:当ES值达到最大时对应的那个基因在排序好的基因列表中所处的位置
LEADING :核心基因集,对ES贡献最大的基因成员;该处有3个统计值:
tags:核心基因集占该基因集中基因总数的百分比;
list:核心基因占所有基因的百分比;
signal:将前两项统计数据合在一起计算出的富集信号强度。
一般认为|NES|>1,NOM p-val<0.05,FDR q-val<0.25的通路是显著富集的。
点击detail查看基因集富集的详细结果,GSEA默认展示前20个基因集结果。以RIG_I_LIKE_RECEPTOR_SIGNALING_PATHWAY通路为例:
打开后,页面如下:
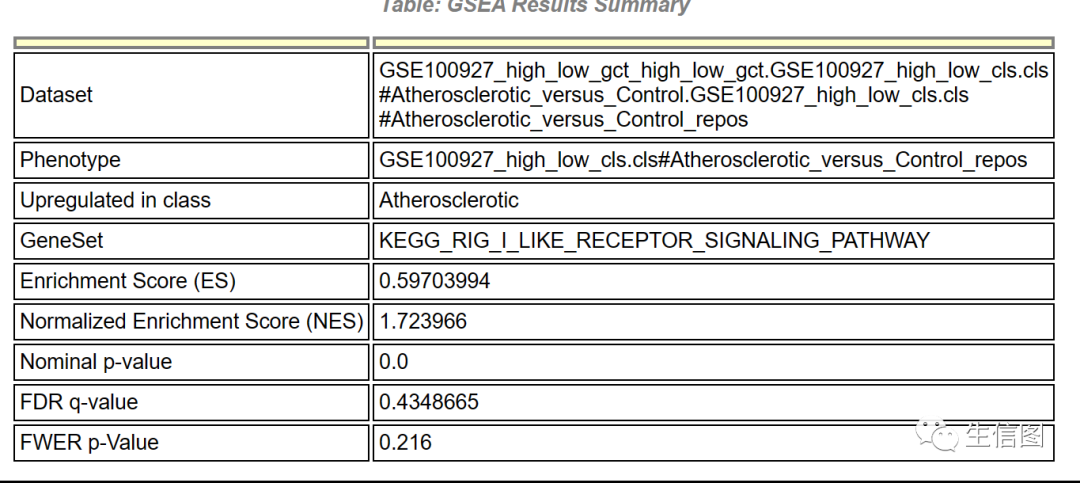
看来又到解读时间了——
如上图,描述的信息为:RIG_I_LIKE_RECEPTOR_SIGNALING_PATHWAY 通路在A组上调(显著富集在 A 的顶端),然后是否显著呢?后面的 ES、NES、pval、FDR 等统计值给出了答案。

再接再厉——
如上图,富集图一共分为上中下 3 部分:
第一部分 ES 折线图:显示了当分析沿着排序基因集按排序计算时,ES 值在计算到每个位置时的展示。最高峰处的ES得分是基因集的 ES 值。
第二部分 hits 图:俗称条形码图,用线条或者 hit 标记了通路基因集中成员出现在基因排序列表中的位置。leading edge subset 就是(0,0)到绿色曲线峰值 ES 出现对应的这部分基因(x轴0到虚线那部分)。
所谓Leading-edge subset,就是对富集得分贡献最大的基因成员。如果ES得分都是正值(如上图所示),那么Leading-edge subset就在峰值ES的左侧,反之则在右侧(底部富集 = A/C 下调表达 = C组高表达)。那么根据本图我们很容易看出,该通路在 A 组高表达。
第三部分是排序后所有基因 rank 值的分布,热图红色部分对应的基因在 A 组高表达,蓝色部分对应的基因在 C组高表达,每个基因对应的信噪比(Signal2noise,前面选择的排序值计算方式)以灰色面积图展示。

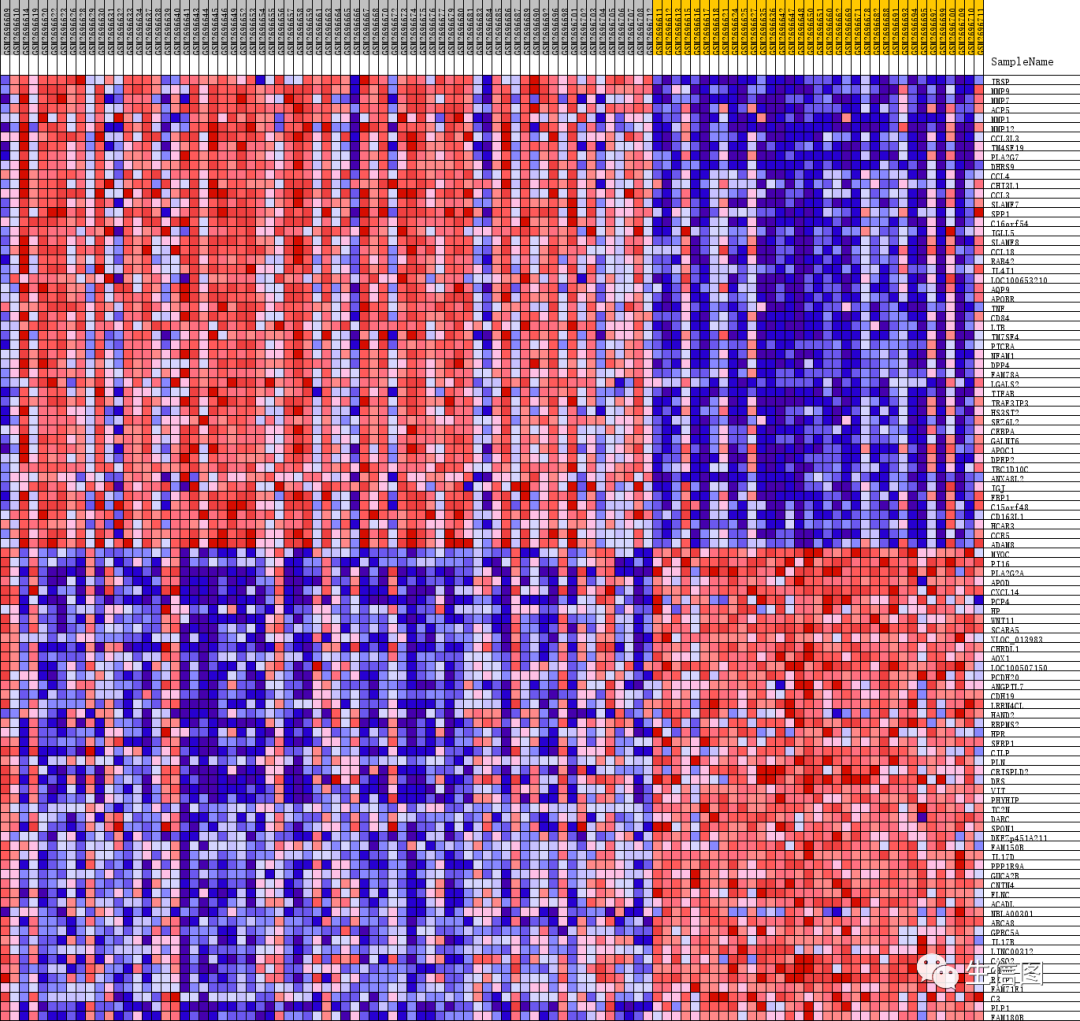
结果中详细给出了该基因集下包含的基因的具体信息和前100个基因使用热图进行展示。
看过小图的解读后是不是发现GSEA也不过如此?下课后赶紧行动起来让小图看看大家的学习成果,欢迎在评论区一起讨论!
有兴趣的朋友可以继续关注小图的微信公众号(生信图)和使用云生信生物信息学平台进行零代码分析。我们下期再见~
欢迎使用:云生信平台 ( http://www.biocloudservice.com/home.html)

|
往期推荐 |
|
|
|
|
|
|